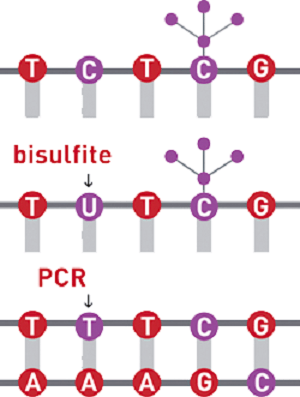
バイサルファイト法によるDNAメチル化解析
DNAのバイサルファイト(亜硫酸水素塩)処理は、DNAメチル化研究において最も一般的に使用されるゴールデンスタンダードの実験手法で、1塩基単位の分解能を有する優れた手法です。
この技術は、メチル化されていないシトシンは、バイサルファイト処理によりウラシルへ化学変換されることに基づく手法です。メチル化されたシトシンは、この化学変換から保護され、その結果、1塩基単位の分解能でのDNAメチル化解析を行うことが可能となります。
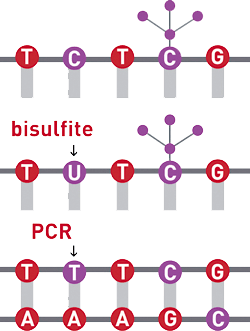
図・亜硫酸水素塩によるDNAの処理によって、シトシン残基はウラシルに変換され、5-メチルシトシン残基は影響を受けないため、配列の違いとして検出できる
バイサルファイト配列決定、パイロシーケンシング、メチル化特異的PCR、高分解能融解曲線分析、マイクロアレイ – 次世代シーケンシングなど、幅広い分析方法で解析可能な、応用範囲の広いDNAメチル化解析方法です。
全ゲノムバイサルファイトシーケンス(WGBS)
WGBSでは次世代シーケンサーを用いて全ゲノム上の網羅的なメチル化状態を検出することが可能です。
ライブラリーの調製中にバイサルファイト処理を行い、シーケンスデータ中のチミンとしてメチル化を検出します。また、NGSで出力されたリード数を比較することによってDNAメチル化レベルを解析できます。
WGBSは探索を目的とした網羅的なアプローチに向いたDNAメチル化解析手法です。
しかし、サンプル当たりのシーケンスデータ量が膨大となり、シーケンスワークフローも煩雑になるという欠点も有しています。
これを解決するために特異的な認識部位を濃縮するなど一部にターゲティングしてバイサルファイト処理を行う手法が選択肢として挙げられます。
もっと詳しく
Premium WGBS kit (全ゲノムバイサルファイトシーケンシング用キット)
(グローバルサイトにリンクします)
Reduced Representation Bisulfite Sequencing (RRBS)
RRBSは、1つまたは複数の制限酵素を用いてゲノムDNA上のCpG配列特異的断片を生成することにより、目的のシーケンス配列を濃縮できるプロトコルです。

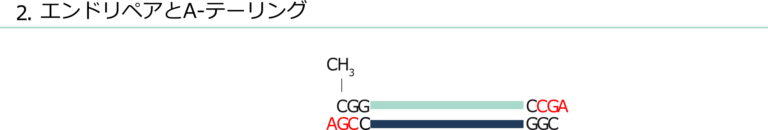
DNAメチル化が生じるCpG領域を含む断片を、CCGGを認識する制限酵素MspIを用いて生成します。

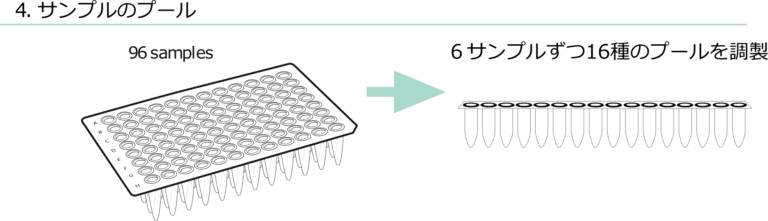
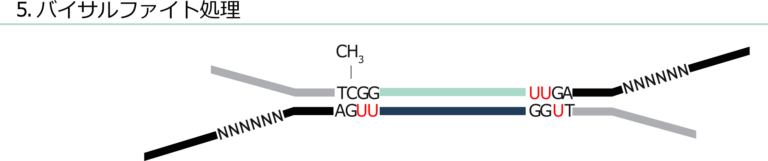
得られたMspI消化ゲノムDNA断片を適切なアダプターにつないでライブラリーを調製し、重亜硫酸塩で処理します。
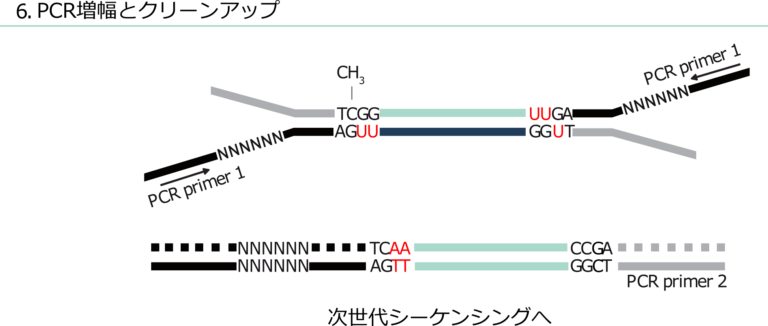
重亜硫酸塩で処理したライブラリーをPCRで増幅して2本鎖にし、NGSで配列決定します。
この手法は、プロモーターおよび反復領域などのメチル化が高い部位に特に有効です。サイズセレクションを行うことによって、実際に決定する配列をさらに少なくすることも可能です。
Diagenode社のReduced Representation Bisulfite Sequencing(RRBS) 用キットはRRBSに必要なCpG部位の濃縮とNGSライブラリ化を行うことが可能です。
Diagenode社の製品は少ないサンプルからでも多くのシーケンスリードを得ることができ、貴重な試料を無駄にしません。
本RRBSキットを用いると、少ないサンプル量から費用対効果の高いDNAメチル化解析ができ、次世代シーケンスにより高い網羅性も併せて獲得することができます。
もっと詳しく
Premium Reduced Representation Bisulfite Sequencing (RRBS) Kit V2(RRBS用キット ver.2)
(グローバルサイトにリンクします)
5-ヒドロキシメチル化シトシン(5-hmC)
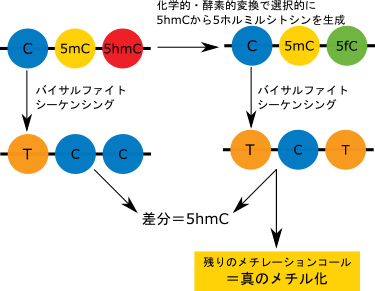
5-ヒドロキシメチル化シトシンはDNA脱メチル化の際の中間産物ですが、エピジェネティクスな遺伝子発現調節の役割を担っていることが分かってきています。
しかしながら、残念ながらバイサルファイト法では効果的にメチル化シトシンとヒドロキシメチル化シトシンを区別できません。
5-ヒドロキシメチル化シトシン(5-hmC)研究には、5-hmCに特異的な抗体を用いてDNA断片の免疫沈降を行うhMeDIP法によって、効果的にゲノムワイドで5-hmCのマッピングを行うことが可能です。
詳しくはMeDIP法のページをご覧ください。
また、5-ヒドロキシメチル化シトシンを酸化処理し、5-ホルミルシトシンに変換した後、バイサルファイト処理・アレイによる解析を行うことによりゲノム全体におけるDNAヒドロキシメチル化のプロファイリングを行うことも近年可能となっています。
製品案内

Premium Reduced Representation Bisulfite Sequencing (RRBS) kit
Reduced Representation Bisulfite Sequencing (RRBS)はCpG部位を含むDNAを濃縮することによって効率よく、単一ヌクレオチドレベルでDNAメチル化を分析することのできる手法です。本キット製品紹介の他、実験手法についてのウェビナーをご覧いただけます。